
|
||||||
|
 | Fusion Gene Summary |
 | Fusion Gene ORF analysis |
 | Fusion Genomic Features |
 | Fusion Protein Features |
 | Fusion Gene Sequence |
 | Fusion Gene PPI analysis |
 | Related Drugs |
 | Related Diseases |
Fusion gene:KIAA0930-ANK3 (FusionGDB2 ID:42012) |
Fusion Gene Summary for KIAA0930-ANK3 |
 Fusion gene summary Fusion gene summary |
| Fusion gene information | Fusion gene name: KIAA0930-ANK3 | Fusion gene ID: 42012 | Hgene | Tgene | Gene symbol | KIAA0930 | ANK3 | Gene ID | 23313 | 288 |
| Gene name | KIAA0930 | ankyrin 3 | |
| Synonyms | C22orf9|LSC3 | ANKYRIN-G|MRT37 | |
| Cytomap | 22q13.31 | 10q21.2 | |
| Type of gene | protein-coding | protein-coding | |
| Description | uncharacterized protein KIAA0930 | ankyrin-3ankyrin 3, node of Ranvier (ankyrin G) | |
| Modification date | 20200313 | 20200313 | |
| UniProtAcc | Q6ICG6 | Q12955 | |
| Ensembl transtripts involved in fusion gene | ENST00000336156, ENST00000391627, ENST00000251993, ENST00000474515, ENST00000443310, ENST00000496226, ENST00000492273, | ENST00000280772, ENST00000373827, ENST00000355288, ENST00000503366, ENST00000510382, ENST00000460468, | |
| Fusion gene scores | * DoF score | 5 X 5 X 4=100 | 25 X 29 X 11=7975 |
| # samples | 6 | 43 | |
| ** MAII score | log2(6/100*10)=-0.736965594166206 possibly effective Gene in Pan-Cancer Fusion Genes (peGinPCFGs). DoF>8 and MAII<0 | log2(43/7975*10)=-4.21307595395013 possibly effective Gene in Pan-Cancer Fusion Genes (peGinPCFGs). DoF>8 and MAII<0 | |
| Context | PubMed: KIAA0930 [Title/Abstract] AND ANK3 [Title/Abstract] AND fusion [Title/Abstract] | ||
| Most frequent breakpoint | KIAA0930(45636521)-ANK3(61898845), # samples:3 | ||
| Anticipated loss of major functional domain due to fusion event. | |||
| * DoF score (Degree of Frequency) = # partners X # break points X # cancer types ** MAII score (Major Active Isofusion Index) = log2(# samples/DoF score*10) |
 Gene ontology of each fusion partner gene with evidence of Inferred from Direct Assay (IDA) from Entrez Gene ontology of each fusion partner gene with evidence of Inferred from Direct Assay (IDA) from Entrez |
| Partner | Gene | GO ID | GO term | PubMed ID |
 Fusion gene breakpoints across KIAA0930 (5'-gene) Fusion gene breakpoints across KIAA0930 (5'-gene)* Click on the image to open the UCSC genome browser with custom track showing this image in a new window. |
 Fusion gene breakpoints across ANK3 (3'-gene) Fusion gene breakpoints across ANK3 (3'-gene)* Click on the image to open the UCSC genome browser with custom track showing this image in a new window. |
 Fusion gene information from two resources (ChiTars 5.0 and ChimerDB 4.0) Fusion gene information from two resources (ChiTars 5.0 and ChimerDB 4.0)* All genome coordinats were lifted-over on hg19. * Click on the break point to see the gene structure around the break point region using the UCSC Genome Browser. |
| Source | Disease | Sample | Hgene | Hchr | Hbp | Hstrand | Tgene | Tchr | Tbp | Tstrand |
| ChimerDB4 | BRCA | TCGA-EW-A1OZ-01A | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| ChimerDB4 | BRCA | TCGA-EW-A1OZ | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| ChimerDB4 | BRCA | TCGA-EW-A1OZ-01A | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| ChimerDB4 | BRCA | TCGA-EW-A1OZ-01A | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
Top |
Fusion Gene ORF analysis for KIAA0930-ANK3 |
 Open reading frame (ORF) analsis of fusion genes based on Ensembl gene isoform structure. Open reading frame (ORF) analsis of fusion genes based on Ensembl gene isoform structure. * Click on the break point to see the gene structure around the break point region using the UCSC Genome Browser. |
| ORF | Henst | Tenst | Hgene | Hchr | Hbp | Hstrand | Tgene | Tchr | Tbp | Tstrand |
| Frame-shift | ENST00000336156 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| Frame-shift | ENST00000336156 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| In-frame | ENST00000336156 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| Frame-shift | ENST00000336156 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| 5CDS-intron | ENST00000336156 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| 5CDS-intron | ENST00000336156 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000391627 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000391627 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000251993 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000251993 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000474515 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000474515 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000443310 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000443310 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000496226 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000496226 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000280772 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000373827 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000503366 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000492273 | ENST00000510382 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000492273 | ENST00000460468 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - |
| Frame-shift | ENST00000336156 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| Frame-shift | ENST00000336156 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| In-frame | ENST00000336156 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| Frame-shift | ENST00000336156 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| 5CDS-intron | ENST00000336156 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| 5CDS-intron | ENST00000336156 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000391627 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000391627 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000391627 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000251993 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000251993 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000251993 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000474515 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000474515 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000474515 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000443310 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000443310 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000443310 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000496226 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000496226 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000496226 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000280772 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000373827 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-3CDS | ENST00000492273 | ENST00000503366 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000492273 | ENST00000510382 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
| intron-intron | ENST00000492273 | ENST00000460468 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - |
 ORFfinder result based on the fusion transcript sequence of in-frame fusion genes. ORFfinder result based on the fusion transcript sequence of in-frame fusion genes. |
| Henst | Tenst | Hgene | Hchr | Hbp | Hstrand | Tgene | Tchr | Tbp | Tstrand | Seq length (transcript) | BP loci (transcript) | Predicted start (transcript) | Predicted stop (transcript) | Seq length (amino acids) |
| ENST00000336156 | KIAA0930 | chr22 | 45636521 | - | ENST00000355288 | ANK3 | chr10 | 61898845 | - | 3276 | 130 | 57 | 3119 | 1020 |
| ENST00000336156 | KIAA0930 | chr22 | 45636520 | - | ENST00000355288 | ANK3 | chr10 | 61898845 | - | 3276 | 130 | 57 | 3119 | 1020 |
 DeepORF prediction of the coding potential based on the fusion transcript sequence of in-frame fusion genes. DeepORF is a coding potential classifier based on convolutional neural network by comparing the real Ribo-seq data. If the no-coding score < 0.5 and coding score > 0.5, then the in-frame fusion transcript is predicted as being likely translated. DeepORF prediction of the coding potential based on the fusion transcript sequence of in-frame fusion genes. DeepORF is a coding potential classifier based on convolutional neural network by comparing the real Ribo-seq data. If the no-coding score < 0.5 and coding score > 0.5, then the in-frame fusion transcript is predicted as being likely translated. |
| Henst | Tenst | Hgene | Hchr | Hbp | Hstrand | Tgene | Tchr | Tbp | Tstrand | No-coding score | Coding score |
| ENST00000336156 | ENST00000355288 | KIAA0930 | chr22 | 45636521 | - | ANK3 | chr10 | 61898845 | - | 0.000478902 | 0.99952114 |
| ENST00000336156 | ENST00000355288 | KIAA0930 | chr22 | 45636520 | - | ANK3 | chr10 | 61898845 | - | 0.000478902 | 0.99952114 |
Top |
Fusion Genomic Features for KIAA0930-ANK3 |
 FusionAI prediction of the potential fusion gene breakpoint based on the pre-mature RNA sequence context (+/- 5kb of individual partner genes, total 20kb length sequence). FusionAI is a fusion gene breakpoint classifier based on convolutional neural network by comparing the fusion positive and negative sequence context of ~ 20K fusion gene data. From here, we can have the relative potentency of the 20K genomic sequence how individual sequnce will be likely used as the gene fusion breakpoints. FusionAI prediction of the potential fusion gene breakpoint based on the pre-mature RNA sequence context (+/- 5kb of individual partner genes, total 20kb length sequence). FusionAI is a fusion gene breakpoint classifier based on convolutional neural network by comparing the fusion positive and negative sequence context of ~ 20K fusion gene data. From here, we can have the relative potentency of the 20K genomic sequence how individual sequnce will be likely used as the gene fusion breakpoints. |
| Hgene | Hchr | Hbp | Hstrand | Tgene | Tchr | Tbp | Tstrand | 1-p | p (fusion gene breakpoint) |
 Distribution of 44 human genomic features loci across 20kb length fusion breakpoint regions. We integrated a total of 44 different types of human genomic feature loci information across five big categories including virus integration sites, repeats, structural variants, chromatin states, and gene expression regulation. More details are in help page. Distribution of 44 human genomic features loci across 20kb length fusion breakpoint regions. We integrated a total of 44 different types of human genomic feature loci information across five big categories including virus integration sites, repeats, structural variants, chromatin states, and gene expression regulation. More details are in help page. |
 Distribution of 44 human genomic features loci across 20kb length fusion breakpoint regions that are ovelapped with the top 1% feature importance score regions. More details are in help page. Distribution of 44 human genomic features loci across 20kb length fusion breakpoint regions that are ovelapped with the top 1% feature importance score regions. More details are in help page. |
Top |
Fusion Protein Features for KIAA0930-ANK3 |
 Go to Go to FGviewer for the breakpoints of chr22:45636521-chr10:61898845 - FGviewer provides the online visualization of the retention search of the protein functional features across DNA, RNA, protein, and pathological levels. |
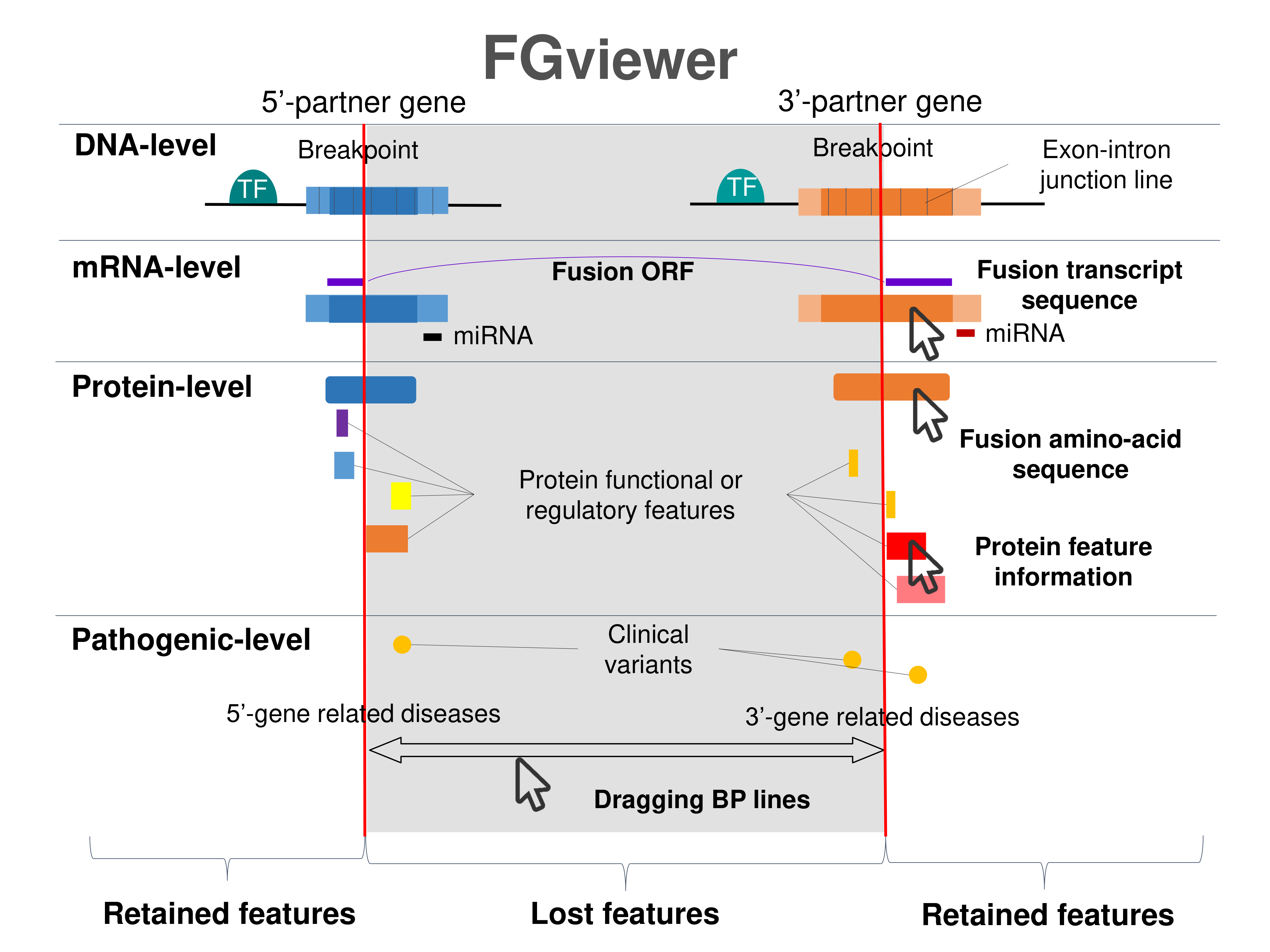 |
 Main function of each fusion partner protein. (from UniProt) Main function of each fusion partner protein. (from UniProt) |
| Hgene | Tgene |
| KIAA0930 | ANK3 |
| FUNCTION: In skeletal muscle, required for costamere localization of DMD and betaDAG1 (By similarity). Membrane-cytoskeleton linker. May participate in the maintenance/targeting of ion channels and cell adhesion molecules at the nodes of Ranvier and axonal initial segments. Regulates KCNA1 channel activity in function of dietary Mg(2+) levels, and thereby contributes to the regulation of renal Mg(2+) reabsorption (PubMed:23903368). {ECO:0000250, ECO:0000269|PubMed:17974005}.; FUNCTION: [Isoform 5]: May be part of a Golgi-specific membrane cytoskeleton in association with beta-spectrin. {ECO:0000305|PubMed:17974005}. |
 Retention analysis result of each fusion partner protein across 39 protein features of UniProt such as six molecule processing features, 13 region features, four site features, six amino acid modification features, two natural variation features, five experimental info features, and 3 secondary structure features. Here, because of limited space for viewing, we only show the protein feature retention information belong to the 13 regional features. All retention annotation result can be downloaded at Retention analysis result of each fusion partner protein across 39 protein features of UniProt such as six molecule processing features, 13 region features, four site features, six amino acid modification features, two natural variation features, five experimental info features, and 3 secondary structure features. Here, because of limited space for viewing, we only show the protein feature retention information belong to the 13 regional features. All retention annotation result can be downloaded at * Minus value of BPloci means that the break pointn is located before the CDS. |
| - In-frame and retained protein feature among the 13 regional features. |
| Partner | Gene | Hbp | Tbp | ENST | Strand | BPexon | TotalExon | Protein feature loci | *BPloci | TotalLen | Protein feature | Protein feature note |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1519_1898 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 2247_2250 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 2393_2396 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3205_3211 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3255_3259 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3482_3487 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3785_3791 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3957_3981 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1519_1898 | 5.333333333333333 | 814.0 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 2247_2250 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 2393_2396 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3205_3211 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3255_3259 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3482_3487 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3785_3791 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3957_3981 | 5.333333333333333 | 814.0 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1519_1898 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 2247_2250 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 2393_2396 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3205_3211 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3255_3259 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3482_3487 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3785_3791 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3957_3981 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1519_1898 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 2247_2250 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 2393_2396 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3205_3211 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3255_3259 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3482_3487 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3785_3791 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3957_3981 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1519_1898 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 2247_2250 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 2393_2396 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3205_3211 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3255_3259 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3482_3487 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3785_3791 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 3957_3981 | 871.3333333333334 | 5447.666666666667 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1519_1898 | 5.333333333333333 | 814.0 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 2247_2250 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 2393_2396 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3205_3211 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3255_3259 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3482_3487 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3785_3791 | 5.333333333333333 | 814.0 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 3957_3981 | 5.333333333333333 | 814.0 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1519_1898 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 2247_2250 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 2393_2396 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3205_3211 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3255_3259 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3482_3487 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3785_3791 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 3957_3981 | 865.3333333333334 | 2277.6666666666665 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1519_1898 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Ser-rich | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 2247_2250 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Thr | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 2393_2396 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3205_3211 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Glu | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3255_3259 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Pro | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3482_3487 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Ser | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3785_3791 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Poly-Asn | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 3957_3981 | 872.3333333333334 | 1808.0 | Compositional bias | Note=Thr-rich | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1141_1288 | 871.3333333333334 | 5447.666666666667 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 4090_4174 | 871.3333333333334 | 5447.666666666667 | Domain | Death | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 984_1139 | 871.3333333333334 | 5447.666666666667 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1141_1288 | 5.333333333333333 | 814.0 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 4090_4174 | 5.333333333333333 | 814.0 | Domain | Death | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 984_1139 | 5.333333333333333 | 814.0 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1141_1288 | 865.3333333333334 | 2277.6666666666665 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 4090_4174 | 865.3333333333334 | 2277.6666666666665 | Domain | Death | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 984_1139 | 865.3333333333334 | 2277.6666666666665 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1141_1288 | 872.3333333333334 | 1808.0 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 4090_4174 | 872.3333333333334 | 1808.0 | Domain | Death | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 984_1139 | 872.3333333333334 | 1808.0 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1141_1288 | 871.3333333333334 | 5447.666666666667 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 4090_4174 | 871.3333333333334 | 5447.666666666667 | Domain | Death | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 984_1139 | 871.3333333333334 | 5447.666666666667 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1141_1288 | 5.333333333333333 | 814.0 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 4090_4174 | 5.333333333333333 | 814.0 | Domain | Death | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 984_1139 | 5.333333333333333 | 814.0 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1141_1288 | 865.3333333333334 | 2277.6666666666665 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 4090_4174 | 865.3333333333334 | 2277.6666666666665 | Domain | Death | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 984_1139 | 865.3333333333334 | 2277.6666666666665 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1141_1288 | 872.3333333333334 | 1808.0 | Domain | ZU5 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 4090_4174 | 872.3333333333334 | 1808.0 | Domain | Death | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 984_1139 | 872.3333333333334 | 1808.0 | Domain | ZU5 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1273_1407 | 871.3333333333334 | 5447.666666666667 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1273_1407 | 5.333333333333333 | 814.0 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1273_1407 | 865.3333333333334 | 2277.6666666666665 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1273_1407 | 872.3333333333334 | 1808.0 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 1273_1407 | 871.3333333333334 | 5447.666666666667 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 1273_1407 | 5.333333333333333 | 814.0 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 1273_1407 | 865.3333333333334 | 2277.6666666666665 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 1273_1407 | 872.3333333333334 | 1808.0 | Region | UPA domain | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 106_135 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 139_168 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 172_201 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 203_230 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 234_263 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 267_296 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 300_329 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 333_362 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 366_395 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 399_428 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 432_461 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 465_494 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 498_527 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 531_560 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 564_593 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 597_626 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 630_659 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 663_692 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 696_725 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 729_758 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 73_102 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 762_791 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000355288 | 0 | 21 | 795_825 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 106_135 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 139_168 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 172_201 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 203_230 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 234_263 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 267_296 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 300_329 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 333_362 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 366_395 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 399_428 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 432_461 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 465_494 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 498_527 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 531_560 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 564_593 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 597_626 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 630_659 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 663_692 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 696_725 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 729_758 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 73_102 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 762_791 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000355288 | 0 | 21 | 795_825 | 5.333333333333333 | 814.0 | Repeat | Note=ANK 23 |
| - In-frame and not-retained protein feature among the 13 regional features. |
| Partner | Gene | Hbp | Tbp | ENST | Strand | BPexon | TotalExon | Protein feature loci | *BPloci | TotalLen | Protein feature | Protein feature note |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 106_135 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 139_168 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 172_201 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 203_230 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 234_263 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 267_296 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 300_329 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 333_362 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 366_395 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 399_428 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 432_461 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 465_494 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 498_527 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 531_560 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 564_593 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 597_626 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 630_659 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 663_692 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 696_725 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 729_758 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 73_102 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 762_791 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000280772 | 22 | 44 | 795_825 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 106_135 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 139_168 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 172_201 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 203_230 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 234_263 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 267_296 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 300_329 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 333_362 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 366_395 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 399_428 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 432_461 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 465_494 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 498_527 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 531_560 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 564_593 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 597_626 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 630_659 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 663_692 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 696_725 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 729_758 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 73_102 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 762_791 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000373827 | 23 | 44 | 795_825 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 106_135 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 139_168 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 172_201 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 203_230 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 234_263 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 267_296 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 300_329 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 333_362 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 366_395 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 399_428 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 432_461 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 465_494 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 498_527 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 531_560 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 564_593 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 597_626 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 630_659 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 663_692 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 696_725 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 729_758 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 73_102 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 762_791 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636520 | chr10:61898845 | ENST00000503366 | 23 | 44 | 795_825 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 106_135 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 139_168 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 172_201 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 203_230 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 234_263 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 267_296 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 300_329 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 333_362 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 366_395 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 399_428 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 432_461 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 465_494 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 498_527 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 531_560 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 564_593 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 597_626 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 630_659 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 663_692 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 696_725 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 729_758 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 73_102 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 762_791 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000280772 | 22 | 44 | 795_825 | 871.3333333333334 | 5447.666666666667 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 106_135 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 139_168 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 172_201 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 203_230 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 234_263 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 267_296 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 300_329 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 333_362 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 366_395 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 399_428 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 432_461 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 465_494 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 498_527 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 531_560 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 564_593 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 597_626 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 630_659 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 663_692 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 696_725 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 729_758 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 73_102 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 762_791 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000373827 | 23 | 44 | 795_825 | 865.3333333333334 | 2277.6666666666665 | Repeat | Note=ANK 23 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 106_135 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 2 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 139_168 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 3 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 172_201 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 4 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 203_230 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 5 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 234_263 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 6 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 267_296 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 7 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 300_329 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 8 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 333_362 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 9 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 366_395 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 10 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 399_428 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 11 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 432_461 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 12 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 465_494 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 13 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 498_527 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 14 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 531_560 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 15 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 564_593 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 16 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 597_626 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 17 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 630_659 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 18 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 663_692 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 19 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 696_725 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 20 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 729_758 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 21 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 73_102 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 1 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 762_791 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 22 | |
| Tgene | ANK3 | chr22:45636521 | chr10:61898845 | ENST00000503366 | 23 | 44 | 795_825 | 872.3333333333334 | 1808.0 | Repeat | Note=ANK 23 |
Top |
Fusion Gene Sequence for KIAA0930-ANK3 |
 For in-frame fusion transcripts, we provide the fusion transcript sequences and fusion amino acid sequences. To have fusion amino acid sequence, we ran ORFfinder and chose the longest ORF among the all predicted ones. For in-frame fusion transcripts, we provide the fusion transcript sequences and fusion amino acid sequences. To have fusion amino acid sequence, we ran ORFfinder and chose the longest ORF among the all predicted ones. |
| >In-frame_ENST00000336156_ENST00000355288_TCGA-EW-A1OZ-01A_KIAA0930_chr22_45636521_-_ANK3_chr10_61898845_length(transcript)=3276nt_BP=130nt CTCCCCGCCGCCGCCGCCCCCGAGCCTGCGGGCGGCGCCGAGGCCGAGGAGCGCTCGCTGCAGCACATGCTGCGTGCCATAGCGGAGGAG CGCGGCCGTCTTAGCCTGCGCCGCGAGGTCTGCGGCCTCGGTGAAGATGCAATGACCGGGGACACAGACAAATATCTTGGGCCACAGGAC CTTAAGGAATTGGGTGATGATTCCCTGCCTGCAGAGGGTTACATGGGCTTTAGTCTCGGAGCGCGTTCTGCCAGCCTCCGCTCCTTCAGT TCGGATAGGTCTTACACCTTGAACAGAAGCTCCTATGCACGGGACAGCATGATGATTGAAGAACTCCTTGTGCCATCCAAAGAGCAGCAT CTAACATTCACAAGGGAATTTGATTCAGATTCTCTTAGACATTACAGCTGGGCTGCAGACACCTTAGACAATGTCAATCTTGTTTCAAGC CCCATTCATTCTGGGTTTCTGGTTAGCTTTATGGTGGACGCGAGAGGGGGCTCCATGAGAGGAAGCCGTCATCACGGGATGAGAATCATC ATTCCTCCACGCAAGTGTACGGCCCCCACTCGAATCACCTGCCGTTTGGTAAAGAGACATAAACTGGCCAACCCACCCCCCATGGTGGAA GGAGAGGGATTAGCCAGTAGGCTGGTAGAAATGGGTCCTGCAGGGGCACAATTTTTAGGCCCTGTCATAGTGGAAATCCCTCACTTTGGG TCCATGAGAGGAAAAGAGAGAGAACTCATTGTTCTTCGAAGTGAAAATGGTGAAACTTGGAAGGAGCATCAGTTTGACAGCAAAAATGAA GATTTAACCGAGTTACTTAATGGCATGGATGAAGAACTTGATAGCCCAGAAGAGTTAGGGAAAAAGCGTATCTGCAGGATTATCACGAAA GATTTCCCCCAGTATTTTGCAGTGGTTTCCCGGATTAAGCAGGAAAGCAACCAGATTGGTCCTGAAGGTGGAATTCTGAGCAGCACCACA GTGCCCCTTGTTCAAGCATCTTTCCCAGAGGGTGCCCTAACTAAAAGAATTCGAGTGGGCCTCCAGGCCCAGCCTGTTCCAGATGAAATT GTGAAAAAGATCCTTGGAAACAAAGCAACTTTTAGCCCAATTGTCACTGTGGAACCAAGAAGACGGAAATTCCATAAACCAATCACAATG ACCATTCCGGTGCCCCCGCCCTCAGGAGAAGGTGTATCCAATGGATACAAAGGGGACACTACACCCAATCTGCGTCTTCTCTGTAGCATT ACAGGGGGCACTTCGCCTGCTCAGTGGGAAGACATCACAGGAACAACTCCTTTGACGTTTATAAAAGATTGTGTCTCCTTTACAACCAAT GTTTCAGCCAGATTTTGGCTTGCAGACTGCCATCAAGTTTTAGAAACTGTGGGGTTAGCCACGCAACTGTACAGAGAATTGATATGTGTT CCATATATGGCCAAGTTTGTTGTTTTTGCCAAAATGAATGATCCCGTAGAATCTTCCTTGCGATGTTTCTGCATGACAGATGACAAAGTG GACAAAACTTTAGAGCAACAAGAGAATTTTGAGGAAGTCGCAAGAAGCAAAGATATTGAGGTTCTGGAAGGAAAACCTATTTATGTTGAT TGTTATGGAAATTTGGCCCCACTTACCAAAGGAGGACAGCAACTTGTTTTTAACTTTTATTCTTTCAAAGAAAATAGACTGCCATTTTCC ATCAAGATTAGAGACACCAGCCAAGAGCCCTGTGGTCGTCTGTCTTTTCTGAAAGAACCAAAGACAACAAAAGGACTGCCTCAAACAGCG GTTTGCAACTTAAATATCACTCTGCCAGCACATAAAAAGATTGAGAAAACAGATAGACGACAGAGCTTCGCATCCTTAGCTTTACGTAAG CGCTACAGCTACTTGACTGAGCCTGGAATGAGTCCACAGAGTCCATGTGAACGGACAGATATCAGGATGGCAATAGTAGCCGATCACCTG GGACTTAGTTGGACAGAACTGGCAAGGGAACTGAATTTTTCAGTGGATGAAATCAATCAAATACGTGTGGAAAATCCAAATTCTTTAATT TCTCAGAGCTTCATGTTATTAAAAAAATGGGTTACCAGAGACGGAAAAAATGCCACAACTGATGCCTTAACTTCGGTCTTGACAAAAATT AATCGAATAGATATAGTGACACTGCTAGAAGGACCAATATTTGATTATGGAAATATTTCAGGCACCAGAAGTTTTGCAGATGAGAACAAT GTTTTCCATGACCCTGTTGATGGTTATCCTTCCCTTCAAGTGGAACTGGAAACCCCCACAGGGTTGCACTACACACCACCTACCCCTTTC CAGCAAGATGATTATTTTAGTGATATCTCTAGCATAGAATCTCCCCTTAGAACCCCTAGTAGACTGAGTGATGGGCTAGTGCCTTCCCAG GGGAACATAGAGCATTCCGCAGATGGACCTCCAGTCGTAACTGCAGAAGACGCTTCCTTAGAAGACAGCAAACTGGAAGACTCAGTGCCT TTAACAGAAATGCCTGAAGCAGTGGATGTAGATGAGAGCCAGTTGGAGAATGTATGTCTGAGTTGGCAGAATGAGACATCAAGTGGAAAC CTAGAGTCCTGCGCTCAAGCTCGAAGAGTAACTGGTGGGTTACTAGATCGACTGGATGACAGCCCTGACCAGTGTAGAGATTCCATTACC TCATATCTCAAAGGAGAAGCTGGCAAATTTGAAGCAAATGGAAGCCATACAGAAATCACTCCAGAAGCAAAGACAAAATCTTACTTTCCA GAATCCCAAAATGATGTAGGAAAACAGAGTACCAAGGAAACTCTGAAACCAAAAATACATGGATCTGGTCATGTTGAAGAACCAGCATCA CCACTAGCAGCATATCAGAAATCTCTAGAAGAAACCAGCAAGCTTATAATAGAAGAGACTAAACCCTGTGTGCCTGTCAGTATGAAAAAG ATGAGTAGGACTTCTCCAGCAGATGGCAAGCCAAGGCTTAGCCTCCATGAAGAAGAGGGGTCCAGTGGGTCTGAGCAAAAGCAGGGAGAA GGTTTTAAGGTGAAAACGAAGAAAGAAATCCGGCATGTGGAAAAGAAGAGCCACTCGTAACAGCGAACGGTCAGTCAAGGATCATAAGTT TTTACTGCCAGTATTGAGAAATTCGTGGAAGAAATGTCAGCAGGAAGTAAAAATTCACCGAGAAGTGTGTGTGTGTTCGCTGCTTCCACA >In-frame_ENST00000336156_ENST00000355288_TCGA-EW-A1OZ-01A_KIAA0930_chr22_45636521_-_ANK3_chr10_61898845_length(amino acids)=1020AA_start in transcript=57_stop in transcript=3119 MQHMLRAIAEERGRLSLRREVCGLGEDAMTGDTDKYLGPQDLKELGDDSLPAEGYMGFSLGARSASLRSFSSDRSYTLNRSSYARDSMMI EELLVPSKEQHLTFTREFDSDSLRHYSWAADTLDNVNLVSSPIHSGFLVSFMVDARGGSMRGSRHHGMRIIIPPRKCTAPTRITCRLVKR HKLANPPPMVEGEGLASRLVEMGPAGAQFLGPVIVEIPHFGSMRGKERELIVLRSENGETWKEHQFDSKNEDLTELLNGMDEELDSPEEL GKKRICRIITKDFPQYFAVVSRIKQESNQIGPEGGILSSTTVPLVQASFPEGALTKRIRVGLQAQPVPDEIVKKILGNKATFSPIVTVEP RRRKFHKPITMTIPVPPPSGEGVSNGYKGDTTPNLRLLCSITGGTSPAQWEDITGTTPLTFIKDCVSFTTNVSARFWLADCHQVLETVGL ATQLYRELICVPYMAKFVVFAKMNDPVESSLRCFCMTDDKVDKTLEQQENFEEVARSKDIEVLEGKPIYVDCYGNLAPLTKGGQQLVFNF YSFKENRLPFSIKIRDTSQEPCGRLSFLKEPKTTKGLPQTAVCNLNITLPAHKKIEKTDRRQSFASLALRKRYSYLTEPGMSPQSPCERT DIRMAIVADHLGLSWTELARELNFSVDEINQIRVENPNSLISQSFMLLKKWVTRDGKNATTDALTSVLTKINRIDIVTLLEGPIFDYGNI SGTRSFADENNVFHDPVDGYPSLQVELETPTGLHYTPPTPFQQDDYFSDISSIESPLRTPSRLSDGLVPSQGNIEHSADGPPVVTAEDAS LEDSKLEDSVPLTEMPEAVDVDESQLENVCLSWQNETSSGNLESCAQARRVTGGLLDRLDDSPDQCRDSITSYLKGEAGKFEANGSHTEI TPEAKTKSYFPESQNDVGKQSTKETLKPKIHGSGHVEEPASPLAAYQKSLEETSKLIIEETKPCVPVSMKKMSRTSPADGKPRLSLHEEE -------------------------------------------------------------- >In-frame_ENST00000336156_ENST00000355288_TCGA-EW-A1OZ_KIAA0930_chr22_45636520_-_ANK3_chr10_61898845_length(transcript)=3276nt_BP=130nt CTCCCCGCCGCCGCCGCCCCCGAGCCTGCGGGCGGCGCCGAGGCCGAGGAGCGCTCGCTGCAGCACATGCTGCGTGCCATAGCGGAGGAG CGCGGCCGTCTTAGCCTGCGCCGCGAGGTCTGCGGCCTCGGTGAAGATGCAATGACCGGGGACACAGACAAATATCTTGGGCCACAGGAC CTTAAGGAATTGGGTGATGATTCCCTGCCTGCAGAGGGTTACATGGGCTTTAGTCTCGGAGCGCGTTCTGCCAGCCTCCGCTCCTTCAGT TCGGATAGGTCTTACACCTTGAACAGAAGCTCCTATGCACGGGACAGCATGATGATTGAAGAACTCCTTGTGCCATCCAAAGAGCAGCAT CTAACATTCACAAGGGAATTTGATTCAGATTCTCTTAGACATTACAGCTGGGCTGCAGACACCTTAGACAATGTCAATCTTGTTTCAAGC CCCATTCATTCTGGGTTTCTGGTTAGCTTTATGGTGGACGCGAGAGGGGGCTCCATGAGAGGAAGCCGTCATCACGGGATGAGAATCATC ATTCCTCCACGCAAGTGTACGGCCCCCACTCGAATCACCTGCCGTTTGGTAAAGAGACATAAACTGGCCAACCCACCCCCCATGGTGGAA GGAGAGGGATTAGCCAGTAGGCTGGTAGAAATGGGTCCTGCAGGGGCACAATTTTTAGGCCCTGTCATAGTGGAAATCCCTCACTTTGGG TCCATGAGAGGAAAAGAGAGAGAACTCATTGTTCTTCGAAGTGAAAATGGTGAAACTTGGAAGGAGCATCAGTTTGACAGCAAAAATGAA GATTTAACCGAGTTACTTAATGGCATGGATGAAGAACTTGATAGCCCAGAAGAGTTAGGGAAAAAGCGTATCTGCAGGATTATCACGAAA GATTTCCCCCAGTATTTTGCAGTGGTTTCCCGGATTAAGCAGGAAAGCAACCAGATTGGTCCTGAAGGTGGAATTCTGAGCAGCACCACA GTGCCCCTTGTTCAAGCATCTTTCCCAGAGGGTGCCCTAACTAAAAGAATTCGAGTGGGCCTCCAGGCCCAGCCTGTTCCAGATGAAATT GTGAAAAAGATCCTTGGAAACAAAGCAACTTTTAGCCCAATTGTCACTGTGGAACCAAGAAGACGGAAATTCCATAAACCAATCACAATG ACCATTCCGGTGCCCCCGCCCTCAGGAGAAGGTGTATCCAATGGATACAAAGGGGACACTACACCCAATCTGCGTCTTCTCTGTAGCATT ACAGGGGGCACTTCGCCTGCTCAGTGGGAAGACATCACAGGAACAACTCCTTTGACGTTTATAAAAGATTGTGTCTCCTTTACAACCAAT GTTTCAGCCAGATTTTGGCTTGCAGACTGCCATCAAGTTTTAGAAACTGTGGGGTTAGCCACGCAACTGTACAGAGAATTGATATGTGTT CCATATATGGCCAAGTTTGTTGTTTTTGCCAAAATGAATGATCCCGTAGAATCTTCCTTGCGATGTTTCTGCATGACAGATGACAAAGTG GACAAAACTTTAGAGCAACAAGAGAATTTTGAGGAAGTCGCAAGAAGCAAAGATATTGAGGTTCTGGAAGGAAAACCTATTTATGTTGAT TGTTATGGAAATTTGGCCCCACTTACCAAAGGAGGACAGCAACTTGTTTTTAACTTTTATTCTTTCAAAGAAAATAGACTGCCATTTTCC ATCAAGATTAGAGACACCAGCCAAGAGCCCTGTGGTCGTCTGTCTTTTCTGAAAGAACCAAAGACAACAAAAGGACTGCCTCAAACAGCG GTTTGCAACTTAAATATCACTCTGCCAGCACATAAAAAGATTGAGAAAACAGATAGACGACAGAGCTTCGCATCCTTAGCTTTACGTAAG CGCTACAGCTACTTGACTGAGCCTGGAATGAGTCCACAGAGTCCATGTGAACGGACAGATATCAGGATGGCAATAGTAGCCGATCACCTG GGACTTAGTTGGACAGAACTGGCAAGGGAACTGAATTTTTCAGTGGATGAAATCAATCAAATACGTGTGGAAAATCCAAATTCTTTAATT TCTCAGAGCTTCATGTTATTAAAAAAATGGGTTACCAGAGACGGAAAAAATGCCACAACTGATGCCTTAACTTCGGTCTTGACAAAAATT AATCGAATAGATATAGTGACACTGCTAGAAGGACCAATATTTGATTATGGAAATATTTCAGGCACCAGAAGTTTTGCAGATGAGAACAAT GTTTTCCATGACCCTGTTGATGGTTATCCTTCCCTTCAAGTGGAACTGGAAACCCCCACAGGGTTGCACTACACACCACCTACCCCTTTC CAGCAAGATGATTATTTTAGTGATATCTCTAGCATAGAATCTCCCCTTAGAACCCCTAGTAGACTGAGTGATGGGCTAGTGCCTTCCCAG GGGAACATAGAGCATTCCGCAGATGGACCTCCAGTCGTAACTGCAGAAGACGCTTCCTTAGAAGACAGCAAACTGGAAGACTCAGTGCCT TTAACAGAAATGCCTGAAGCAGTGGATGTAGATGAGAGCCAGTTGGAGAATGTATGTCTGAGTTGGCAGAATGAGACATCAAGTGGAAAC CTAGAGTCCTGCGCTCAAGCTCGAAGAGTAACTGGTGGGTTACTAGATCGACTGGATGACAGCCCTGACCAGTGTAGAGATTCCATTACC TCATATCTCAAAGGAGAAGCTGGCAAATTTGAAGCAAATGGAAGCCATACAGAAATCACTCCAGAAGCAAAGACAAAATCTTACTTTCCA GAATCCCAAAATGATGTAGGAAAACAGAGTACCAAGGAAACTCTGAAACCAAAAATACATGGATCTGGTCATGTTGAAGAACCAGCATCA CCACTAGCAGCATATCAGAAATCTCTAGAAGAAACCAGCAAGCTTATAATAGAAGAGACTAAACCCTGTGTGCCTGTCAGTATGAAAAAG ATGAGTAGGACTTCTCCAGCAGATGGCAAGCCAAGGCTTAGCCTCCATGAAGAAGAGGGGTCCAGTGGGTCTGAGCAAAAGCAGGGAGAA GGTTTTAAGGTGAAAACGAAGAAAGAAATCCGGCATGTGGAAAAGAAGAGCCACTCGTAACAGCGAACGGTCAGTCAAGGATCATAAGTT TTTACTGCCAGTATTGAGAAATTCGTGGAAGAAATGTCAGCAGGAAGTAAAAATTCACCGAGAAGTGTGTGTGTGTTCGCTGCTTCCACA >In-frame_ENST00000336156_ENST00000355288_TCGA-EW-A1OZ_KIAA0930_chr22_45636520_-_ANK3_chr10_61898845_length(amino acids)=1020AA_start in transcript=57_stop in transcript=3119 MQHMLRAIAEERGRLSLRREVCGLGEDAMTGDTDKYLGPQDLKELGDDSLPAEGYMGFSLGARSASLRSFSSDRSYTLNRSSYARDSMMI EELLVPSKEQHLTFTREFDSDSLRHYSWAADTLDNVNLVSSPIHSGFLVSFMVDARGGSMRGSRHHGMRIIIPPRKCTAPTRITCRLVKR HKLANPPPMVEGEGLASRLVEMGPAGAQFLGPVIVEIPHFGSMRGKERELIVLRSENGETWKEHQFDSKNEDLTELLNGMDEELDSPEEL GKKRICRIITKDFPQYFAVVSRIKQESNQIGPEGGILSSTTVPLVQASFPEGALTKRIRVGLQAQPVPDEIVKKILGNKATFSPIVTVEP RRRKFHKPITMTIPVPPPSGEGVSNGYKGDTTPNLRLLCSITGGTSPAQWEDITGTTPLTFIKDCVSFTTNVSARFWLADCHQVLETVGL ATQLYRELICVPYMAKFVVFAKMNDPVESSLRCFCMTDDKVDKTLEQQENFEEVARSKDIEVLEGKPIYVDCYGNLAPLTKGGQQLVFNF YSFKENRLPFSIKIRDTSQEPCGRLSFLKEPKTTKGLPQTAVCNLNITLPAHKKIEKTDRRQSFASLALRKRYSYLTEPGMSPQSPCERT DIRMAIVADHLGLSWTELARELNFSVDEINQIRVENPNSLISQSFMLLKKWVTRDGKNATTDALTSVLTKINRIDIVTLLEGPIFDYGNI SGTRSFADENNVFHDPVDGYPSLQVELETPTGLHYTPPTPFQQDDYFSDISSIESPLRTPSRLSDGLVPSQGNIEHSADGPPVVTAEDAS LEDSKLEDSVPLTEMPEAVDVDESQLENVCLSWQNETSSGNLESCAQARRVTGGLLDRLDDSPDQCRDSITSYLKGEAGKFEANGSHTEI TPEAKTKSYFPESQNDVGKQSTKETLKPKIHGSGHVEEPASPLAAYQKSLEETSKLIIEETKPCVPVSMKKMSRTSPADGKPRLSLHEEE -------------------------------------------------------------- |
Top |
Fusion Gene PPI Analysis for KIAA0930-ANK3 |
 Go to ChiPPI (Chimeric Protein-Protein interactions) to see the chimeric PPI interaction in Go to ChiPPI (Chimeric Protein-Protein interactions) to see the chimeric PPI interaction in |
 Protein-protein interactors with each fusion partner protein in wild-type (BIOGRID-3.4.160) Protein-protein interactors with each fusion partner protein in wild-type (BIOGRID-3.4.160) |
| Hgene | Hgene's interactors | Tgene | Tgene's interactors |
 - Retained PPIs in in-frame fusion. - Retained PPIs in in-frame fusion. |
| Partner | Gene | Hbp | Tbp | ENST | Strand | BPexon | TotalExon | Protein feature loci | *BPloci | TotalLen | Still interaction with |
 - Lost PPIs in in-frame fusion. - Lost PPIs in in-frame fusion. |
| Partner | Gene | Hbp | Tbp | ENST | Strand | BPexon | TotalExon | Protein feature loci | *BPloci | TotalLen | Interaction lost with |
 - Retained PPIs, but lost function due to frame-shift fusion. - Retained PPIs, but lost function due to frame-shift fusion. |
| Partner | Gene | Hbp | Tbp | ENST | Strand | BPexon | TotalExon | Protein feature loci | *BPloci | TotalLen | Interaction lost with |
Top |
Related Drugs for KIAA0930-ANK3 |
 Drugs targeting genes involved in this fusion gene. Drugs targeting genes involved in this fusion gene. (DrugBank Version 5.1.8 2021-05-08) |
| Partner | Gene | UniProtAcc | DrugBank ID | Drug name | Drug activity | Drug type | Drug status |
Top |
Related Diseases for KIAA0930-ANK3 |
 Diseases associated with fusion partners. Diseases associated with fusion partners. (DisGeNet 4.0) |
| Partner | Gene | Disease ID | Disease name | # pubmeds | Source |
| Tgene | ANK3 | C0005586 | Bipolar Disorder | 8 | CTD_human;PSYGENET |
| Tgene | ANK3 | C0005587 | Depression, Bipolar | 3 | CTD_human |
| Tgene | ANK3 | C0024713 | Manic Disorder | 3 | CTD_human |
| Tgene | ANK3 | C0036341 | Schizophrenia | 3 | PSYGENET |
| Tgene | ANK3 | C0338831 | Manic | 3 | CTD_human |
| Tgene | ANK3 | C0033975 | Psychotic Disorders | 2 | PSYGENET |
| Tgene | ANK3 | C0525045 | Mood Disorders | 2 | PSYGENET |
| Tgene | ANK3 | C0015923 | Fetal Alcohol Syndrome | 1 | CTD_human |
| Tgene | ANK3 | C0024121 | Lung Neoplasms | 1 | CTD_human |
| Tgene | ANK3 | C0033300 | Progeria | 1 | CTD_human |
| Tgene | ANK3 | C0038220 | Status Epilepticus | 1 | CTD_human |
| Tgene | ANK3 | C0178417 | Anhedonia | 1 | PSYGENET |
| Tgene | ANK3 | C0242379 | Malignant neoplasm of lung | 1 | CTD_human |
| Tgene | ANK3 | C0270823 | Petit mal status | 1 | CTD_human |
| Tgene | ANK3 | C0311335 | Grand Mal Status Epilepticus | 1 | CTD_human |
| Tgene | ANK3 | C0349204 | Nonorganic psychosis | 1 | PSYGENET |
| Tgene | ANK3 | C0393734 | Complex Partial Status Epilepticus | 1 | CTD_human |
| Tgene | ANK3 | C0751522 | Status Epilepticus, Subclinical | 1 | CTD_human |
| Tgene | ANK3 | C0751523 | Non-Convulsive Status Epilepticus | 1 | CTD_human |
| Tgene | ANK3 | C0751524 | Simple Partial Status Epilepticus | 1 | CTD_human |
| Tgene | ANK3 | C0814154 | Alcohol Related Neurodevelopmental Disorder | 1 | CTD_human |
| Tgene | ANK3 | C2985290 | Fetal Alcohol Spectrum Disorders | 1 | CTD_human |
| Tgene | ANK3 | C3146244 | Alcohol Related Birth Defect | 1 | CTD_human |
| Tgene | ANK3 | C3661483 | Partial Fetal Alcohol Syndrome | 1 | CTD_human |
| Tgene | ANK3 | C3809672 | MENTAL RETARDATION, AUTOSOMAL RECESSIVE 37 | 1 | CTD_human;GENOMICS_ENGLAND;ORPHANET |
